b. 福建农林大学, 植物保护学院, 福州 350002;
c. 福建农林大学, 农学院, 福州 350002;
d. 福建农林大学, 生命科学学院, 福州 350002
b. College of Plant Protection, Fujian Agriculture and Forestry University, Fuzhou 350002, China;
c. College of Agriculture, Fujian Agriculture and Forestry University, Fuzhou 350002, China;
d. College of Life Science, Fujian Agriculture and Forestry University, Fuzhou 350002, China
Flor提出“基因对基因”假说,认为对于病原的每个无毒基因(Avr),宿主都有1个相应的抗性基因(R基因),这2个基因产物互作激活宿主的防御反应, 如超敏反应(hypersensitive response, HR)[1]。根据结构域基序,R基因的编码产物R蛋白分为5类[2], 第一类含有丝氨酸-苏氨酸激酶结构域和十四烷基化结构域;第二类包含LRR (leucine-rich repeat)结构域、NBS (nucleotide-binding site)结构域和位于N端的亮氨酸拉链(leucine zipper)或卷曲螺旋(coiled coil)序列;第三类和第二类相似,但N端序列为TIR (toll and Interleukin 1 receptor)结构域;第四类具有跨膜结构域和胞外LRR结构域,但是缺失NBS; 第五类含有跨膜结构域、胞外LRR结构域和丝氨酸-苏氨酸激酶结构域。在这些结构域中,NBS结构域是这类蛋白家族的关键结构域,可能通过与核苷酸结合或水解来影响R蛋白的功能。
三裂叶薯(Ipomoea triloba)是栽培甘薯(I. batatas)的二倍体近缘野生种,主要分布于我国台湾、广东和美洲热带等地,具有抗旱、抗病等优良性状[3-4]。研究表明[5-6],野生种三裂叶薯可作为克服种间杂交不亲和性,通过胚胎培养获得杂种的重要材料。三裂叶薯基因组测序于2018年完成[7],本研究基于测序结果对其进行CDS (coding domain sequence)区域预测,检索其中的NBS-ARC家族基因并进行结构分析、染色体定位、保守结构域分析和进化树构建,为三裂叶薯的抗病研究及甘薯的抗性育种提供参考。
1 材料和方法 1.1 材料三裂叶薯(Ipomoea triloba)全基因组序列从https://www.ncbi.nlm.nih.gov/genome/?term=Ipomoea triloba L.下载,共16条染色体的DNA序列。
1.2 基因注释通过snap程序应用拟南芥(At.hmm)、线虫(Ce.hmm)和水稻(Os.hmm)的HMM模型对三裂叶薯全基因组序列CDS区域进行检索,所得作为训练三裂叶薯特异HMM模型的文件(Itl.hmm), 后以Itl.hmm作为检索工具预测属于三裂叶薯基因组的CDS区域,并得到其全基因组蛋白质序列。
1.3 基因预测通过pfam下载含有NB-ARC家族序列信息的HMM文件(PF00931),作为检索序列对三裂叶薯的全基因组蛋白质序列进行NB-ARC结构域搜索。从中选取可用序列(E-value≤1E-60),用Sam- tools构建三裂叶薯的NB-ARC蛋白本地数据文件,同时,用Clustal Omega进行比对并用hmmbuild建立三裂叶薯特异HMM模型,并再次检索全基因组蛋白序列预测NB-ARC结构域,得到三裂叶薯高特异的NB-ARC序列信息。最后导入NCBI Conserved Domains Tool和Interproscan进行筛选,剔除结构域缺失严重序列,得到三裂叶薯NB-ARC基因家族蛋白质序列数据库。
1.4 保守结构域分类从Pfam中下载TIR HMMs、RPW8 HMMs和LRR HMMs模型,合并后用hmmpress程序建立TRL.hmm模型,随后通过hmmscan对三裂叶薯的NBS-LRR家族基因信息库进行结构域预测,并结合Interproscan查看结果对TIR/RPW8/LRR结构域进行类型分类和统计。运用Pepcoil与Paircoil2对三裂叶薯NBS-LRR家族基因编码的蛋白质序列中的CC结构域进行预测和检测。
1.5 染色体定位对三裂叶薯16条染色体上的NBS-LRR家族基因位置信息进行统计,根据其在染色体上的位置分成上、中、下3个部分,每个部分按照N、NL、CN、CNL、TN、TNL和RN共7个类型进行分类统计。
1.6 基序分析将三裂叶薯NBS-LRR家族基因进行分类整理后,从中筛选出CC-NBS-LRR、TIR-NBS-LRR和RPW8-NBS共3种NBS亚家族类型的氨基酸序列。保守基序的分析与识别通过MEME进行,并将运行后得到的.xml文件利用TBtools进行处理。
1.7 进化树构建将筛选得到的3种NBS-LRR亚家族类型编码的CC-NBS-LRR、TIR-NBS-LRR和RPW8-NBS氨基酸序列利用Clustal Omega程序进行多序列比对, 随后使用Gblocks提取保守序列,进一步用Jalview手动矫正。以比对结果为基础,应用MEGA X软件, Maximum Likehood法模式为WAG with Freqs. (+F) model,校验参数Bootstrap=500运行生成三裂叶薯NBS-LRR基因家族系统进化树。
2 结果和分析 2.1 NB-ARC基因鉴别及其分类采用snap程序对三裂叶薯全基因组序列进行CDS区域识别预测,经筛选后获得282个NB-ARC家族基因,占全基因组基因数(98025)的0.288%。根据TIR/RPW8/LRR结构域和CC结构域,这些基因可进一步分为N (NBS)、NL (NBS-LRR)、CN (CC- NBS)、CNL (CC-NBS-LRR)、TN (TNL-LRR)、TNL (TNL-NBS-LRR)和RN (RPW8-NBS)共7个亚家族类型(表 1),分别有80、83、28、57、10、23和1个基因。不同基因的NBS/LRR结构域重复数不同, 在染色体中的分布位置也存在差异。此外,还含有马铃薯抗X病毒和类似蛋白的RX-CC_like结构域(coiled coil domain of the potato virus X resistance protein and similar proteins),即Cx结构域,与Pepcoil程序得到的CC结构域不同。根据基因结构域的特点和差异, 将NBS/LRR基因类型进一步分为40个小类(表 1)。
| 表 1 三裂叶薯NBS-LRR基因的数量和分类 Table 1 Number and type of NBS-LRR genes of Ipomoea triloba |
NBS-LRR家族基因在三裂叶薯16条染色体上的分布差异明显(表 2),不同的亚家族类型,CN型、CNL型、N型、NL型、TN型、TNL型和RN型在各染色体上的数量和位置较不均匀。在第16号染色体仅有1个NBS-LRR家族基因,而在第15号染色体多达65个。NBS-LRR家族基因在染色体的位置也有差异,第4、13和14号染色体的NBS-LRR家族基因主要位于染色体的中部和上部,而在第7、11和15号染色体则以中部和下部居多(表 2)。
| 表 2 三裂叶薯NBS-LRR家族基因在染色体上的分布 Table 2 Chromosomal location of NBS-LRR family genes of Ipomoea triloba |
NBS-LRR家族基因在各染色体上分布形式也存在明显不同,有些是以单基因分布于染色体,而有些则以基因簇的形式存在。三裂叶薯每条染色体上的基因簇数量也存在较大差异,如第15号染色体的基因簇最多,有10个;第16号染色体则没有基因簇(表 3)。所有染色体总共有55个基因簇,包含了179个NBS-LRR基因,占NBS-LRR家族基因总基因数(282)的63.5%。
| 表 3 三裂叶薯NBS-LRR基因家族基因簇统计表 Table 3 Statistics of NBS-LRR family gene clusters in Ipomoea triloba |
分别将三裂叶薯NBS-LRR蛋白家族中CNL和TNL亚家族氨基酸序列信息利用MEME程序检测, 得到15个相似度较高的结构域。CNL亚家族氨基酸序列(共57条)结构域的分布(图 1)有以下规律: motif 9-motif 10-motif 1 (P-loop)-motif 4 (RNBS-A)- motif 2 (kinase 2)-motif 15 (RNBS-C)-motif 6 (GLPL)-motif 8-motif 3 (RNBS-D)-motif 12-motif 7-motif 11-motif 14-motif 11-motif 5-motif 13。TNL亚家族氨基酸序列(共22条)结构域的分布有以下规律(图 2):motif 11 (TIR-1)-motif 3 (TIR-2)-motif 1 (TIR-3)-motif 13 (TIR-4)-motif 5 (P-loop)-motif 10- motif 2 (kinase 2)-motif 9 (RNBS-B)-motif 4 (RNBS- C)-motif 14 (GLPL)-motif 6-motif 8 (RNBS-D)-motif 7 (MHDV)-motif 12-motif 15-motif 12-motif 15。
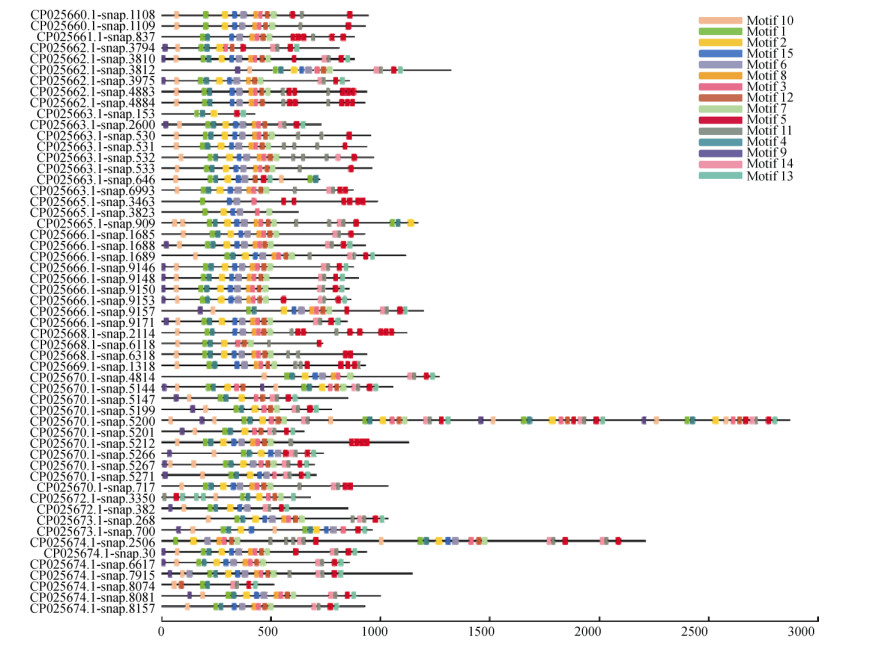
|
图 1 三裂叶薯NBS-LRR基因家族中CNL亚家族蛋白保守结构域分布 Fig. 1 Distribution of conservative domains of CNL subfamily proteins in NBS-LRR gene family of Ipomoea triloba |
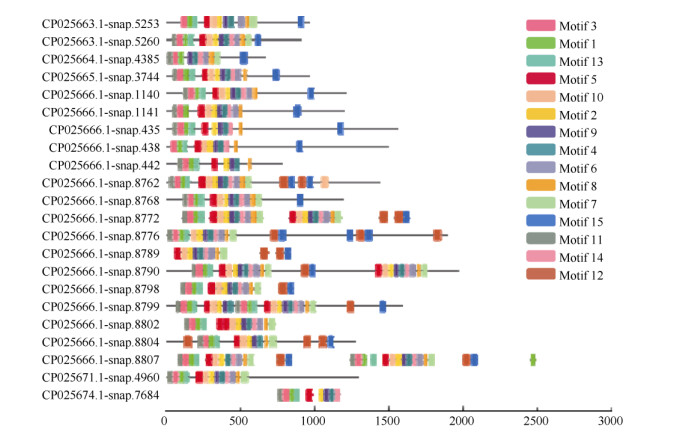
|
图 2 三裂叶薯TNL亚家族蛋白保守结构域分布 Fig. 2 Distribution of conservative domain of TNL subfamily proteins in Ipomoea triloba |
在植物的NBS-LRR蛋白家族中NB-ARC区域相对保守,通常有8个保守基序[8]: P-loop、RNBS-A、Kinase2、RNBS-B、RNBS-C、GLPL、RNBS-D和MHDV。对三裂叶薯NBS-LRR家族氨基酸序列利用Clustal Omega筛选出20条序列进行多重比对, 结果表明,具有5个保守性较高的结构域[9-11](图 3), 分别为P-loop (Kinase 1)、Kinase 2、RNBS-B、GLPL和MHDV。其中P-loop、Kinase 2、RNBS-B、GLPL、MHDV最保守的氨基酸序列分别为SIV GMGGI GKTT+AR++F (下划线为氨基酸保守性较强序列)、R+LLVLDDV、GS+I+LTTR++++L、AGGLPLAL+ V+G、GKMHDLV++MG。
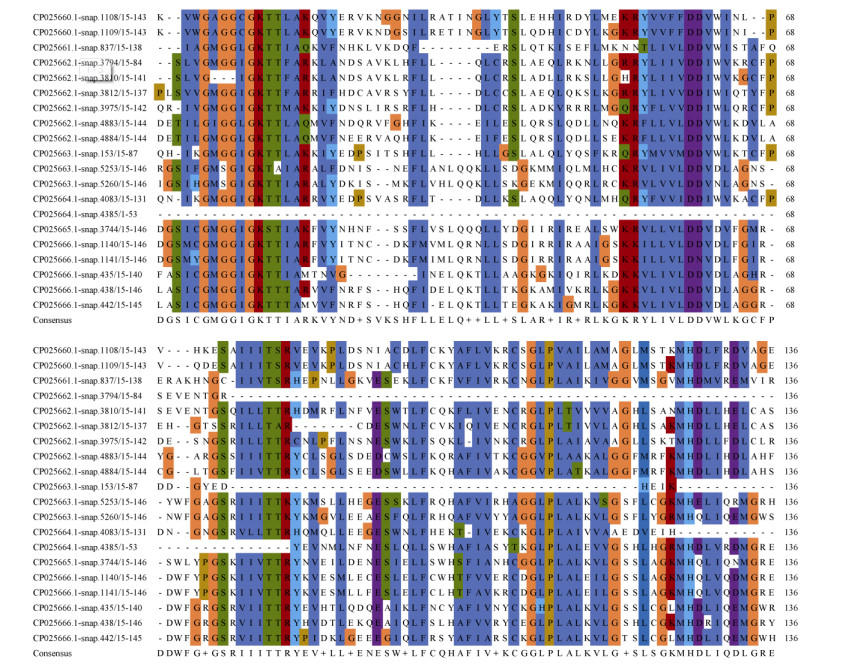
|
图 3 三裂叶薯CNL和TNL亚家族NB-ARC保守性分析 Fig. 3 Conservation analysis of the NB-ARC in CNL and TNL subfamilies in Ipomoea triloba |
根据MEME结构域搜索结果,对CNL和TNL亚家族基因结构域进行基因识别和定位[12]。从表 4可见,TNL和CNL亚家族中分别有11和7个保守结构域,其中TNL亚家族NB-ARC结构域中保守基序分别为P-loop、Kinase 2、RNBS-B、RNBS-C、GLPL、RNBS-D和MHDV,缺失RNBS-A保守基序。CNL亚家族NB-ARC结构域保守基序分别为P-loop、RNBS-A、Kinase 2、RNBS-C、GLPL、RNBS- D和MHDV,缺失RNBS-B保守基序。TNL和CNL亚家族中共有的保守基序分别为P-loop (Kinase 1)、Kinase 2、RNBS-C、GLPL、RNBS-D和MHDV。此外,在TNL亚家族中TIR结构域检测到4个保守基序(TIR 1~TIR 4)[13]。
| 表 4 三裂叶薯NBS-LRR家族蛋白保守结构域和氨基酸保守性分析 Table 4 Conservative domains and amino acids of NBS-LRR family proteins in Ipomoea triloba |
将三裂叶薯的NBS-LRR家族蛋白中CC/TIR/ RPW8/NBS/LRR结构域序列分别提取,使用MEGA X构建进化树(图 4),可见有3个明显的分支,分别为CNL型(蓝色)、TNL型(紫色)和RN型(黄色)。进化树分支中有些基因分支路径很长,如CP025666.1-snap.8798、CP025670.1-snap.5147等, 推测这类基因的“祖先”基因在较早时即已发生分化,相应的基因序列也发生了较大的变化。有些基因序列的分支距离较近, 如CP025666.1-snap.1140和CP025666.1-snap.1141、CP025663.1-snap.531和CP025663.1-snap.532,说明这些变化发生的时间较晚。
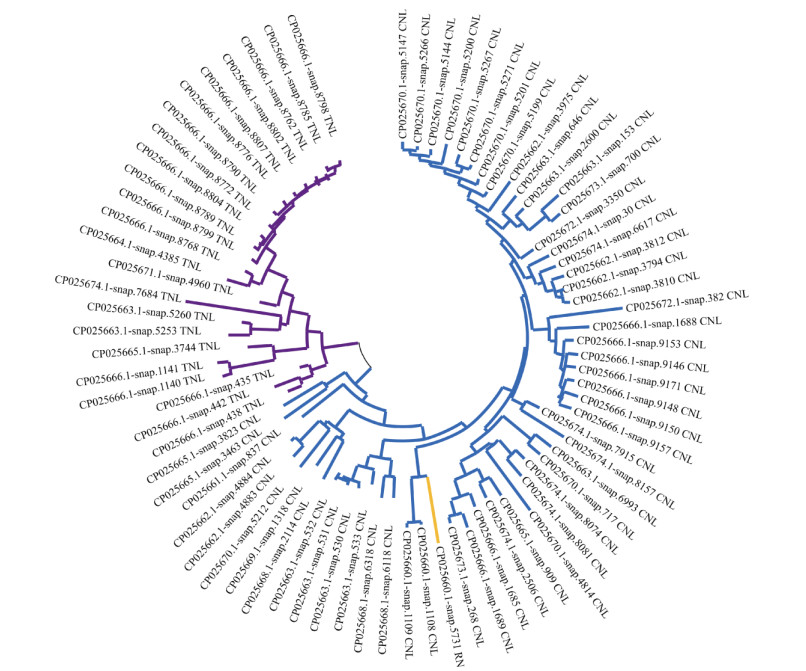
|
图 4 三裂叶薯NBS-LRR家族基因系统进化树 Fig. 4 Phylogenetic tree of NBS-LRR family genes in Ipomoea triloba |
植物R基因在长期的抗病过程中监控识别病原微生物产生的无毒基因(Avr),从而引发植物细胞过敏性坏死,产生免疫反应。R基因与Avr基因间互作模式包括直接作用、间接作用和转录调控[14]。通过克隆植物体内相关的抗病R基因,研究其与病原物的互作模式与机制,或将其遗传转化到目标作物中, 增强作物的抗病能力,有利于提高作物产量, 保障生产安全。
甘薯在生产上面临着许多病害的威胁,如南方薯区的蔓割病、薯瘟病,北方薯区的茎线虫病、黑斑病、根腐病等,以及最近时有发生的茎腐病等病害,都严重影响甘薯生产的安全。甘薯抗性是产量和品质的坚实保证[15],因而抗性育种是甘薯育种的重要方向。甘薯种质资源是甘薯育种工作的基础[16], 然而,甘薯种质资源在新品种育种工作中存在利用率低、育成品种遗传背景狭窄、优秀资源筛选困难等问题[17-18]。因此,如何充分发掘、利用野生种质资源,拓宽甘薯遗传背景,对于选育具有突破性的甘薯新品种具有重要意义。研究表明,甘薯与其近缘野生种三裂叶薯杂交不亲和,无法直接利用其抗性基因,但应用原生质体细胞融合法可以获得三裂叶薯和甘薯的种间体细胞杂种植株,或者可以通过克隆其抗性基因,通过遗传转化提高栽培种甘薯的抗性水平,以充分发挥三裂叶薯基因资源在甘薯育种中的巨大潜力[5, 19-20]。
值得注意的是,甘薯栽培种为同源异源六倍体,三浅裂野牵牛(I. trifida)存在二倍体、四倍体和六倍体,一套染色体均为15条,但数据库中三裂叶薯基因组的染色体数为16,本文即以三裂叶薯16条染色体的全基因组序列为研究对象开展了相关的研究,研究结果有待于与甘薯和三浅裂野牵牛基因组进行进一步的比较,分析它们之间的异同之处,将有利于甘薯的进化研究和育种工作。
对作物全基因组NBS-LRR基因进行鉴定分析, 有利于其抗性资源的应用[21],本研究对三裂叶薯全基因组蛋白序列进行了预测,并鉴定、筛选了NBS- LRR类抗病基因,获得NBS-LRR家族基因的数量、在染色体上定位与分布,分析了基因结构域特点, 构建了进化树,为进一步发掘其抗性基因资源,研究甘薯抗病分子机制,提高甘薯抗性育种水平提供了参考。
| [1] |
ZHENG X W, ZHAI W X, LI X B, et al. NBS-LRR resistance gene homologues in rice[J]. Sci China (Ser C), 2001, 31(3): 253-262. 郑先武, 翟文学, 李晓兵, 等. 水稻NBS-LRR类R基因同源序列[J]. 中国科学(C辑), 2001, 31(1): 43-51. DOI:10.1007/BF02879332 |
| [2] |
MARTIN G B, BOGDANOVE A J, SESSA G. Understanding the functions of plant disease resistance proteins[J]. Annu Rev Plant Biol, 2003, 54: 23-61. DOI:10.1146/annurev.arplant.54.031902.135035 |
| [3] |
SONG X, SHEN Y D, HUANG Q Q, et al. Effect of aqueous extracts of 3 plants (Ipomoea cairica, Ipomoea triloba and Ipomoea digitata) on seed germination and seedling growth of radish, cabbage, mustard and asparagus lettuce[J]. J Trop Biol, 2013, 4(1): 50-55. 宋鑫, 沈奕德, 黄乔乔, 等. 五爪金龙、三裂叶薯和七爪龙水浸液对4种作物种子萌发与幼苗生长的影响[J]. 热带生物学报, 2013, 4(1): 50-55. DOI:10.3969/j.issn.1674-7054.2013.01.009 |
| [4] |
SHI X W, HE L H, JIAO J H, et al. Genome-wide characterization of MYB transcription factors and response to abiotic stresses in Ipomoea triloba[J]. J Nucl Agric Sci, 2018, 32(7): 1338-1348. 石晓雯, 贺立恒, 焦晋华, 等. 甘薯二倍体近缘野生种三裂叶薯MYB转录因子全基因组分析及逆境胁迫响应[J]. 核农学报, 2018, 32(7): 1338-1348. DOI:10.11869/j.issn.100-8551.2018.07.1338 |
| [5] |
WANG J X, LU S Y, ZHOU H Y, et al. The second report of studies on overcoming the interspecific incompatibility and hybrid abortion between series A and B in the section Batalas of the genus Ipomoea[J]. Acta Agron Sin, 1998, 24(2): 139-146. 王家旭, 陆漱韵, 周海鹰, 等. 克服甘薯组(section Batatas)种间杂交不亲和性研究再报[J]. 作物学报, 1998, 24(2): 139-146. |
| [6] |
WANG J X, LU S Y. Primary report of studies on overcoming the interspecific incompatibility and hybrid abortion between series A and B in the section Batatas of genus Ipomoea[J]. Acta Agron Sin, 1993, 19(2): 111-118, 195. 王家旭, 陆漱韵. 克服甘薯组(section Batatas)种间杂交不亲和性研究初报[J]. 作物学报, 1993, 19(2): 111-118, 195. |
| [7] |
WU S, LAU K H, CAO Q H, et al. Genome sequences of two diploid wild relatives of cultivated sweetpotato reveal targets for genetic improvement[J]. Nat Commun, 2018, 9(1): 4580. DOI:10.1038/s41467-018-06983-8 |
| [8] |
LIU Z C, XIE J M, WANG H P, et al. Identification and expression profiling analysis of NBS-LRR genes involved in Fusarium oxysporum f.sp. conglutinans resistance in cabbage[J/OL]. 3 Biotechnol, 2019, 9: 202. doi: 10.1007/s13205-019-1714-8.
|
| [9] |
MEYERS B C, KOZIK A, GRIEGO A, et al. Genome-wide analysis of NBS-LRR-encoding genes in Arabidopsis[J]. Plant Cell, 2003, 15(4): 809-834. DOI:10.1105/tpc.009308 |
| [10] |
KOHLER A, RINALDI C, DUPLESSIS S, et al. Genome-wide identification of NBS resistance genes in Populus trichocarpa[J]. Plant Mol Biol, 2008, 66(6): 619-636. DOI:10.1007/s11103-008-9293-9 |
| [11] |
LOZANO R, PONCE O, RAMIREZ M, et al. Genome-wide identification and mapping of NBS-encoding resistance genes in Solanum tuberosum group Phureja[J]. PLoS One, 2012, 7(4): e34775. DOI:10.1371/journal.pone.0034775 |
| [12] |
LI T G, WANG B L, YIN C M, et al. The Gossypium hirsutum TIR-NBS-LRR gene GhDSC1 mediates resistance against verticillium wilt[J]. Mol Plant Pathol, 2019, 20(6): 857-876. DOI:10.1111/mpp.12797 |
| [13] |
MEYERS B C, MORGANTE M, MICHELMORE R W. TIR-X and TIR-NBS proteins:Two new families related to disease resistance TIR-NBS-LRR proteins encoded in Arabidopsis and other plant genomes[J]. Plant J, 2002, 32(1): 77-92. DOI:10.1046/j.1365-313X.2002.01404.x |
| [14] |
HE F, WANG C C, WANG F Q, et al. Interaction mechanism between plant resistance gene and pathogen avirulence gene[J]. Chin J Cell Biol, 2011, 33(9): 1037-1044. 何锋, 王长春, 王锋青, 等. 植物抗病基因(R)与病原物无毒基因(Avr)相互作用机制的研究进展[J]. 中国细胞生物学学报, 2011, 33(9): 1037-1044. |
| [15] |
CHEN G S, ZHOU Y F, Lin S, et al. Isolation and sequence analysis of NBS-type resistance gene analogues in sweet potato (Ipomoea batatas (L.) Lam.)[J]. J Trop Subtrop Bot, 2006, 14(5): 359-365. 陈观水, 周以飞, 林生, 等. 甘薯NBS类抗病基因类似物的分离与序列分析[J]. 热带亚热带植物学报, 2006, 14(5): 359-365. DOI:10.3969/j.issn.1005-3395.2006.05.001 |
| [16] |
FANF B P, ZHANG X J, CHEN J Y, et al. The history and status of sweet potato germplasm research in China[J]. Guangdong Agric Sci, 2004(S1): 3-5. 房伯平, 张雄坚, 陈景益, 等. 我国甘薯种质资源研究的历史与现状[J]. 广东农业科学, 2004(S1): 3-5. DOI:10.3969/j.issn.1004-874X.2004.z1.001 |
| [17] |
ZHAO D L, TANG J, CAO Q H, et al. Preliminary study on construction of core collection of sweet potato germplasms in China[J]. Acta Agric Jiangxi, 2012, 24(10): 36-39. 赵冬兰, 唐君, 曹清河, 等. 中国甘薯种质资源核心种质构建初探[J]. 江西农业学报, 2012, 24(10): 36-39. DOI:10.3969/j.issn.1001-8581.2012.10.011 |
| [18] |
ZHANG M S, LIU Z, QI J L, et al. Methods of comprehensive evaluation for drought resistance in sweet potato cultivars[J]. J Trop Subtrop Bot, 2005, 13(6): 469-474. 张明生, 刘志, 戚金亮, 等. 甘薯品种抗旱适应性综合评价的方法研究[J]. 热带亚热带植物学报, 2005, 13(6): 469-474. DOI:10.3969/j.issn.1005-3395.2005.06.002 |
| [19] |
ZHANG B Y, LIU Q C, ZHAI H, et al. Effective regeneration of interspecific somatic hybrid plants between sweet potato and its kindred species[J]. Sci Agric Sin, 1999, 32(6): 23-27. 张冰玉, 刘庆昌, 翟红, 等. 甘薯及其近缘野生种种间体细胞杂种植株的有效再生[J]. 中国农业科学, 1999, 32(6): 23-27. DOI:10.3321/j.issn:0578-1752.1999.06.004 |
| [20] |
WANG J S, LIU Q C, MENG X X, et al. Regeneration of interspecific somatic hybrid between sweetpotato and its wild relative Ipomoea triloba[J]. J Agric Biotechnol, 2003, 11(1): 40-43. 王晶珊, 刘庆昌, 孟祥霞, 等. 甘薯和近缘野生种Ipomoea triloba的种间体细胞杂种植株再生[J]. 农业生物技术学报, 2003, 11(1): 40-43. DOI:10.3969/j.issn.1674-7968.2003.01.009 |
| [21] |
LIU M Y, LI W M, WU W, et al. Identification and characterization of NBS-encoding disease resistance genes in Musa acuminata genome[J]. J Trop Subtrop Bot,, 2014, 22(5): 486-494. 刘梦雅, 李伟明, 吴伟, 等. 小果野蕉(Musa acuminata)全基因组NBS抗病基因的鉴定与分析[J]. 热带亚热带植物学报, 2014, 22(5): 486-494. DOI:10.3969/j.issn.1005-3395.2014.05.010 |
 2020, Vol. 28
2020, Vol. 28



